- PCA는 데이터의 숨겨진 패턴을 드러내줍니다.
- Feature Space의 데이터 분포 중 가장 넓게 분포한 것부터 찾아주기 때문에 X Feature들만으로는 보기 어려운 패턴을 찾을 수 있습니다.
- X 인자들의 분포 패턴에 Y feature를 얹어서 그려봅시다.
- Feature engineering을 위한 실마리를 찾고자 합니다.
1. 데이터
-
이번 예시는 현업 데이터를 그대로 가져왔습니다.
-
데이터 공개나 자세한 설명이 어려운 점 양해바랍니다.
-
X data: 22개의 인자, 250만 줄 이상.
-
Y data: 1개의 인자, 불균형 Regression 문제.
-
가장 큰 어려움 중 하나는 Y 데이터의 불균형이 극심하다는 점입니다.
-
Y > 0.1이 전체의 0.8%, Y > 0.5가 전체의 0.06%에 불과합니다.
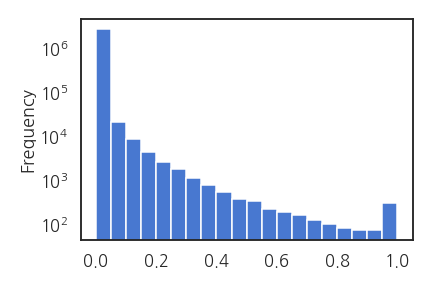
2. 전처리
2.1. outlier 제거
-
사전 작업을 통해 데이터의 outlier가 극심함을 알고 있습니다.
-
신뢰성있는 작업을 위해 outlier를 제거합니다.
-
대개 Q1과 Q3에서 IQR의 1.5배를 넘어서는 데이터를 outlier로 간주합니다.
-
정규분포에서 2.7$$\sigma$$에 해당하는 지점으로, 전체 데이터의 0.7% 가량이 outlier로 처리됩니다.
-
유사하게 데이터의 전체 비율 중 양 끝단을 제거하는 방식을 사용하겠습니다.
-
단, 제거 비율을 입력하면서 Y 데이터의 불균형에 미치는 영향을 확인하고, X 인자 중 0부터 시작하는 것은 이상치가 아니므로 제거하지 않습니다.
-
이상치 제거 함수를 작성합니다.
1 | def cut_quantile(x, lower, upper): |
- 데이터의 극단으로부터 1% 이상과 0.1% 이상을 제거합니다.
1 | # 1% 제거 |
-
확인 결과, 1% 제거시 전체의 16% 제거, 0.1%는 전체의 2.1%를 제거합니다.
-
의도와 달리 너무 많이 제거됩니다.
-
모든 인자가 극단에 있는 데이터가 드물다는 의미입니다.
-
X 이상치를 날린 후의 분포를 확인합니다. 시각화 코드는 생략합니다.
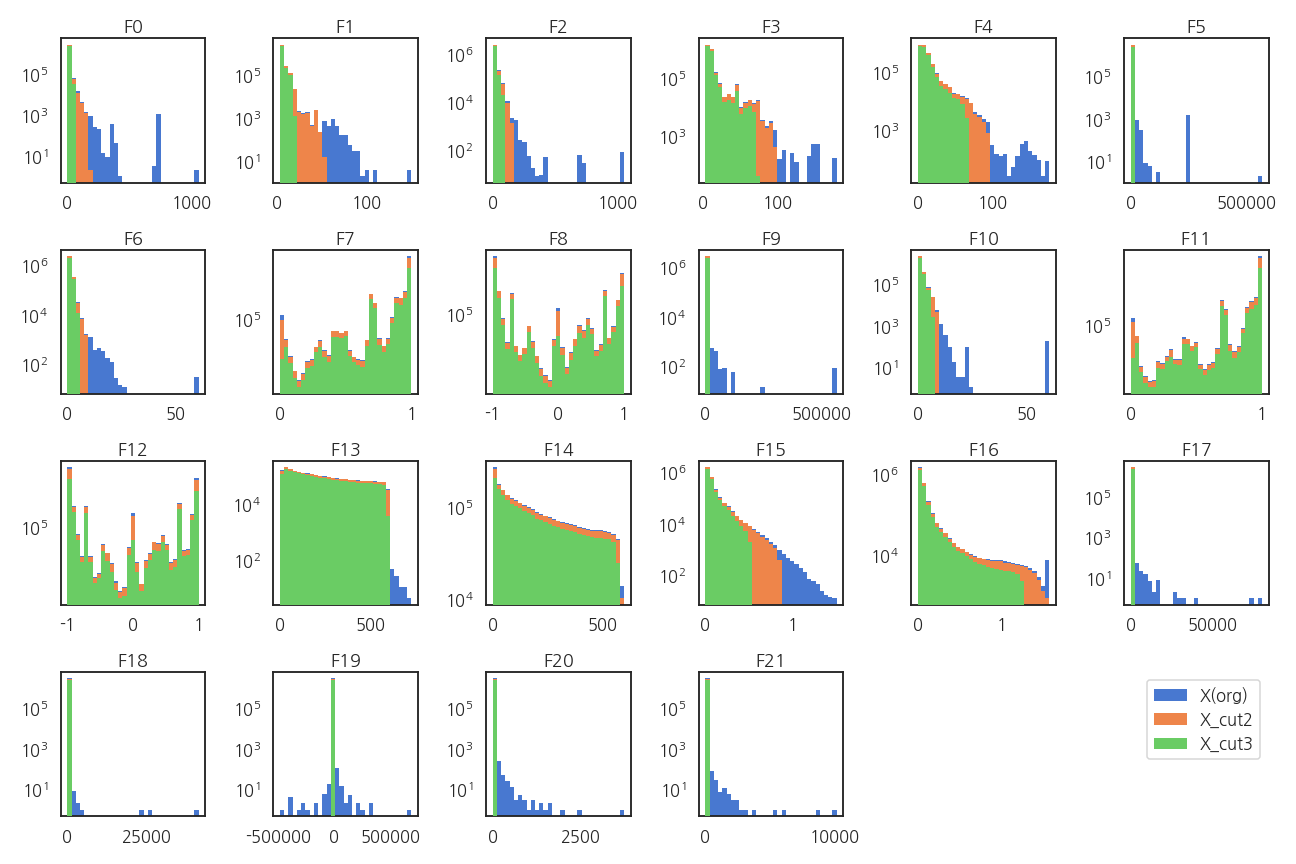
-
Y 인자는 무사한지 걱정이 됩니다.
-
X 이상치 제거로 Y 인자의 분포가 어떻게 변했는지 확인합니다.
-
히스토그램을 얻어서 구간별 데이터를 저장한 뒤 이상치 제거 전과의 차이를 봅니다.
1 | def plot_hist_delta(y1, y2, filename=None, bins=20): |
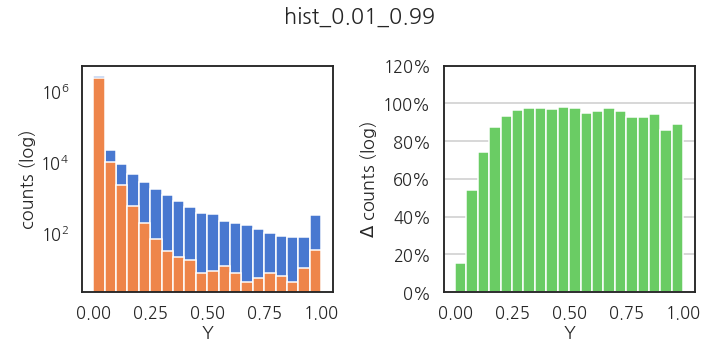
- 1% 제거시: y 인자가 0 부근일 때를 제외하고 거의 다 날아갑니다.
1 | plot_hist_delta(Y, Y_cut2, "hist_0.01_0.99") |
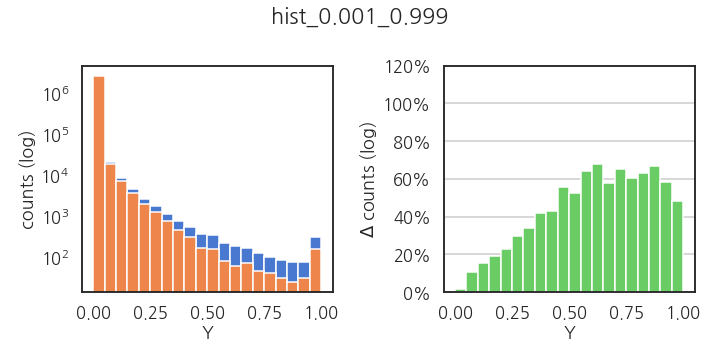
- 0.1% 제거시: 조금 낫지만 귀한 y > 0.5에서 손실률이 더 큽니다.
1 | plot_hist_delta(Y, Y_cut2, "hist_0.001_0.999") |
2.2. scaling
- PCA는 feature space의 분포를 기준으로 주성분을 결정합니다.
- 따라서 인자간 scaling이 매우 중요하며, 잘못되면 틀린 결론이 유도됩니다.
- 양 끝점을 0~1로 지정하는 MinMaxScaling을 수행합니다.
- 시험삼아 Std. Scaling을 섞어봤는데 무의미한 결과가 얻어지더군요.
1 | from sklearn import preprocessing |
3. PCA
3.1. explained variance ratio
- 이번 작업의 목적이 차원 축소는 아닙니다.
- 그러나 PCA가 효율적으로 수행되었는지 확인하기 위해 분산설명력을 확인합니다.
1 | def calc_evr(pca, filename=None): |
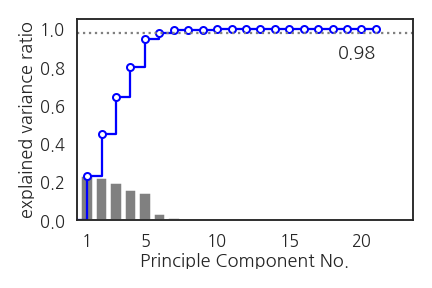
- 22개의 인자 중 처음 여섯 개만으로 98%의 분산이 설명됩니다.
- PCA가 상당히 효과적으로 진행되었음을 알 수 있습니다.
3.2. eigenvector
- PC1 ~ PC6까지 어떤 feature들로 구성되었는지 확인합니다.
1 | def calc_topn(pca, pca_cevr, filename="mm"): |
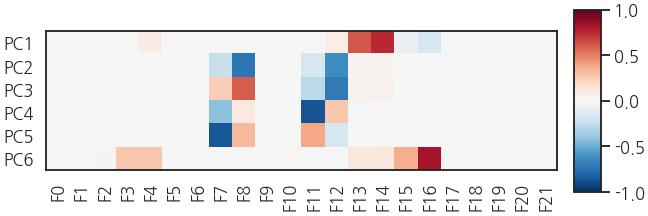
- 제법 흥미로운 결과가 나왔습니다.
- PC1과 PC2~PC5, PC6 세 개의 그룹으로 나눌 수 있는데 각 그룹에 사용된 인자가 독립적입니다.
- PC2~PC5도 언뜻 보기에 중구난방이지만 일종의 각도에 해당하는 인자이기 때문에 모두 물리적으로 의미가 있어보입니다.
- PC1~PC6까지 6차원 공간의 데이터 분포를 그리면 뭔가 보일 것 같습니다.
3.3. data distribution in PC space
- PC 공간상의 데이터 분포를 보면 좋겠는데, 6차원은 2차원에 표현이 안됩니다.
- 6차원에서 두 개씩 뽑아서 2차원 그림 21개로 표현합니다.
- 데이터가 250만개가 넘습니다. 250만개 x 21개 > 5천만개를 넣으면 메모리가 걱정입니다.
- 작은 그림을 그려서 파일로 저장한 후 큰 그림에 붙여넣습니다.
1 | def plot_PCn_hist(X_pca, Y, PCn, filename=None): |
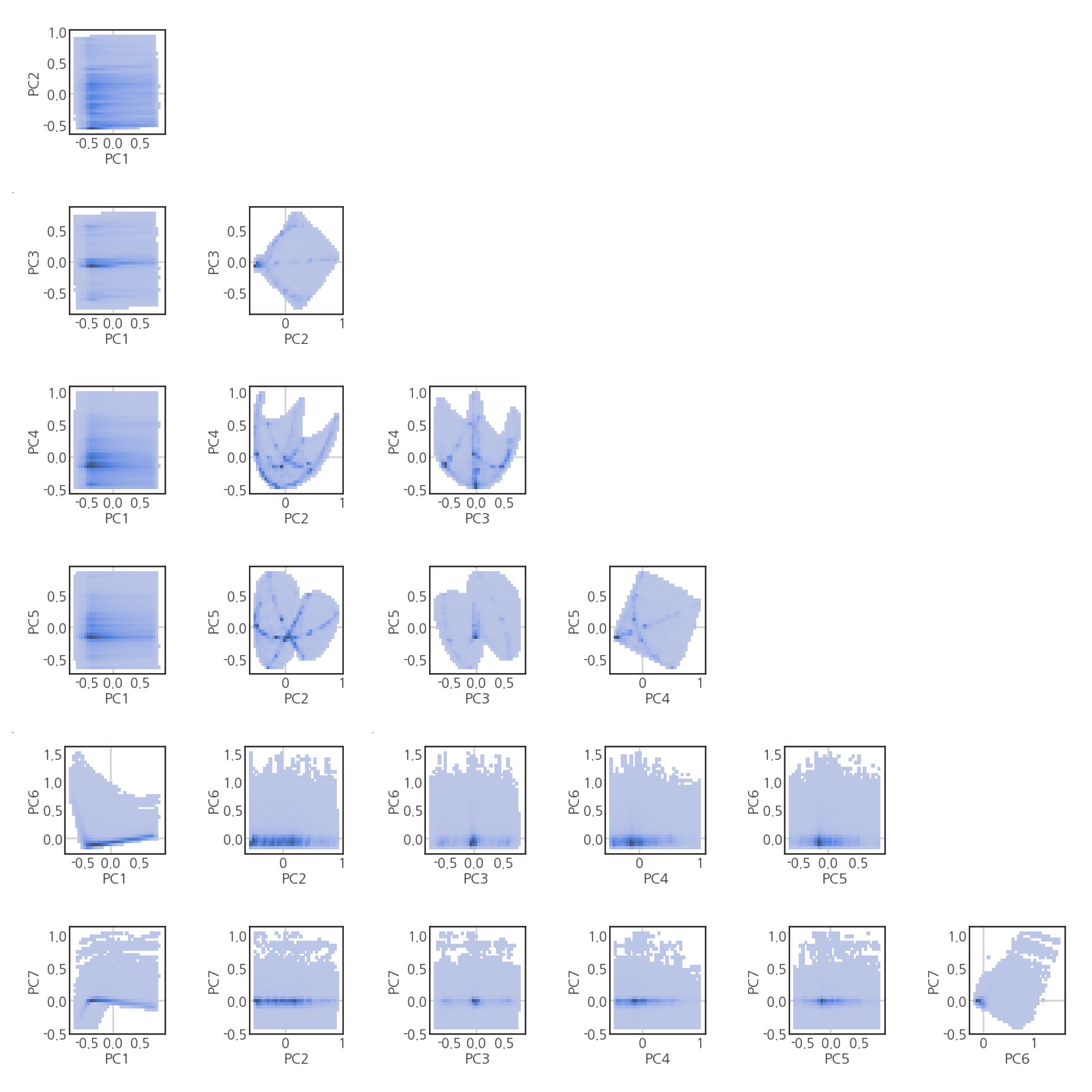
- 특정 지점의 데이터 밀도가 높습니다.
- 곳곳에 점이나 선 같은 패턴이 보입니다.
3.4. Y 인자 overlap
- 데이터가 어떻게 분포하는지 알았으니 Y 인자와는 어떻게 관련됐는지 보겠습니다.
- scatter plot을 그리고 color에 Y 인자를 지정, colormap에 inferno를 지정합니다.
- 대부분의 데이터가 Y ~ 0이라서 그냥 그리면 큰 Y 값들이 묻혀 보이지 않습니다.
- scatter plot을 그리기 전 데이터를 Y값 기준으로 정렬하면 보입니다.
1 | def plot_PCn(X_pca, Y, PCn, filename=None): |

- 데이터 밀도가 높은 곳에 Y값이 큰 데이터가 놓여 있습니다.
- 패턴이 명확해서 살짝 들뜨면서도 이걸 어떻게 분류하나 싶어집니다.
3.5. 3D Plot
-
2차원 그림으로 두 변수 사이의 관계는 파악이 되지만, 여전히 저 그림들이 6D로 어떻게 맞물리는지는 머리가 좀 아픕니다.
-
제한적이나마 3D 그림을 그려봅니다.
-
PC1, PC2, PC3를 골라서 3D Plot을 그려보겠습니다.
-
근데 3D 그림엔 한 가지 고려할 사항이 있습니다.
-
자연스러우려면, 멀리 있는 데이터가 가까이 있는 데이터에 가려져야 합니다.
-
matplotlib은 시선의 방향을 파악하고 거기에 맞게 데이터를 정렬해 줍니다.
-
interactive toy model로 확인합시다.
-
jupyter notebook (lab)에 ipympl이 설치돼있다면
%matplotlib widget으로 interactive를 사용할 수 있습니다.
1 | %matplotlib widget |
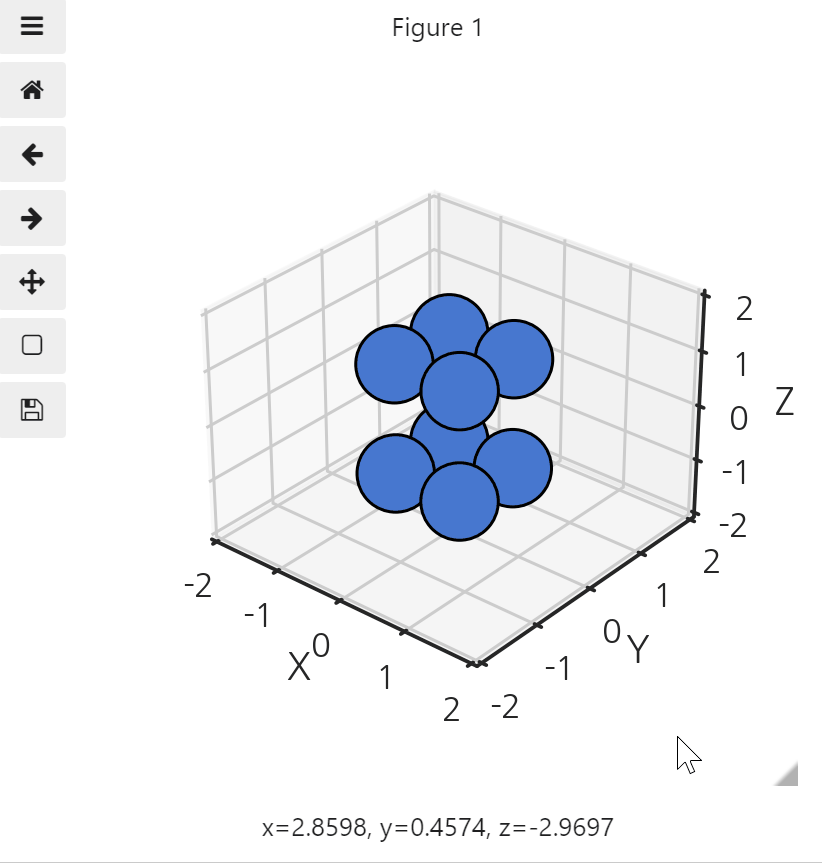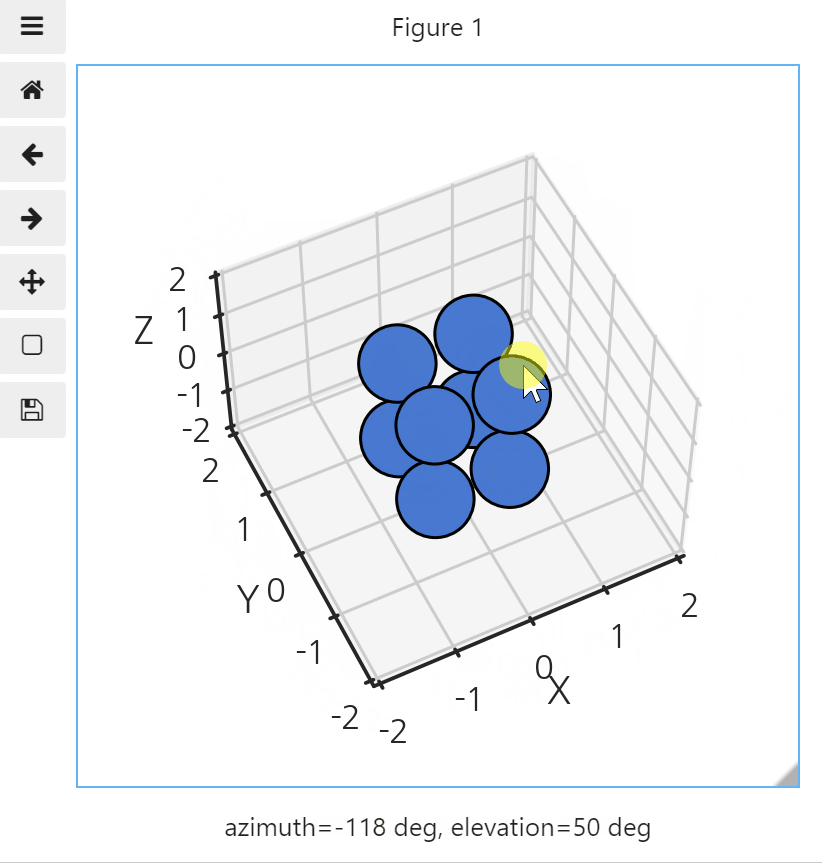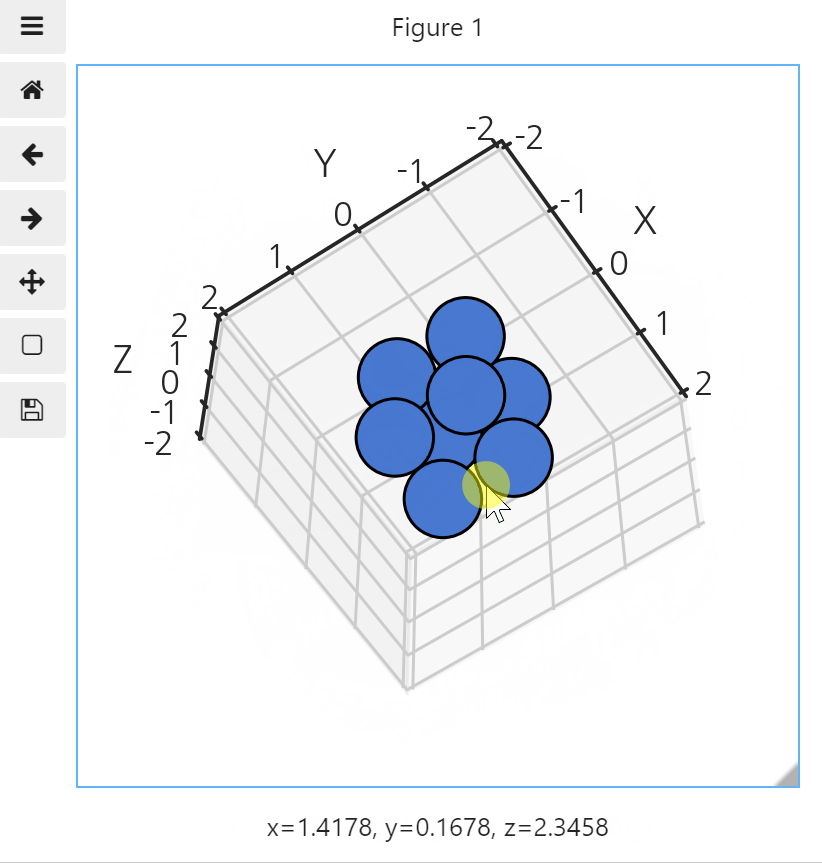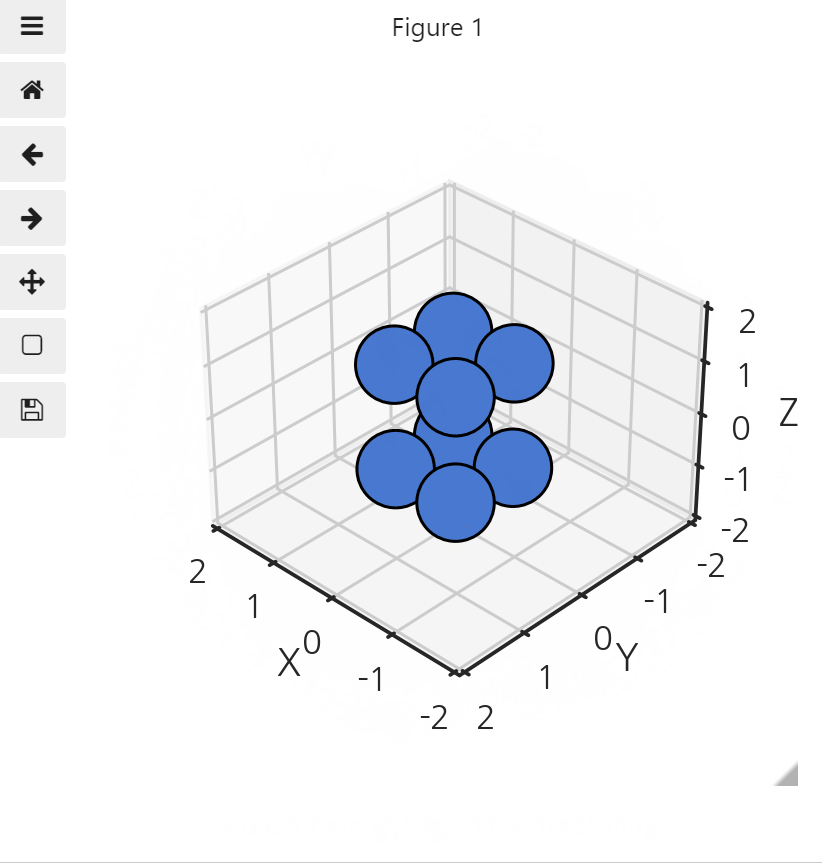
-
그런데 조금 억울합니다.
-
예전엔 시선에 자동으로 맞춰주는 기능이 없었거든요.
-
수동으로 데이터를 시선에 맞춰 정렬해줘야만 했습니다.
-
시선의 방향이 azimuthal angle, elevation(polar angle)으로 지정되어 있습니다.
-
내적을 통해 시선의 방향에 가까운 순으로 데이터를 정렬합니다.
-
확인을 위해 시선의 방향에 가까운 순으로 colormap을 입힙니다.
1 | %matplotlib inline |
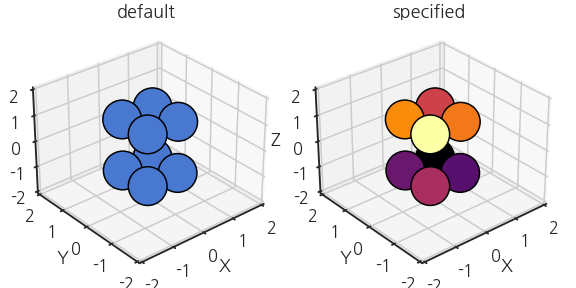
- 본 목적으로 돌아옵니다.
- PC1, PC2, PC3를 각기 x, y, z축으로 scatter plot을 그립니다.
- Y 인자값을 색상으로 입히는데, 앞에 있는 데이터에 뒤의 데이터가 가립니다.
- Y값이 큰 데이터의 위치를 파악하기 위해 $$Y > threshold$$를 적용하여 조금씩 그립니다.
1 | fig = plt.figure(figsize=(20, 5)) |
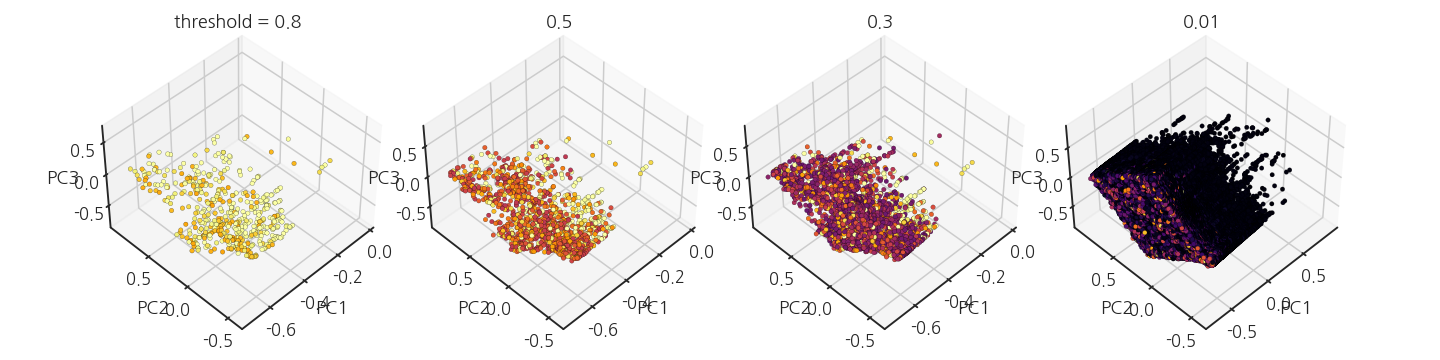
4. 결론
- PCA 결과를 가능한 그림으로 표현했습니다.
- X인자로 수행한 PCA의 데이터 분포를 파악하고, Y값과의 연관성을 파악했습니다.
- 데이터를 추가로 분석할 아이디어가 조금 생겼습니다.
- 좋은 결과로 이어지면 좋겠습니다.
