Essence
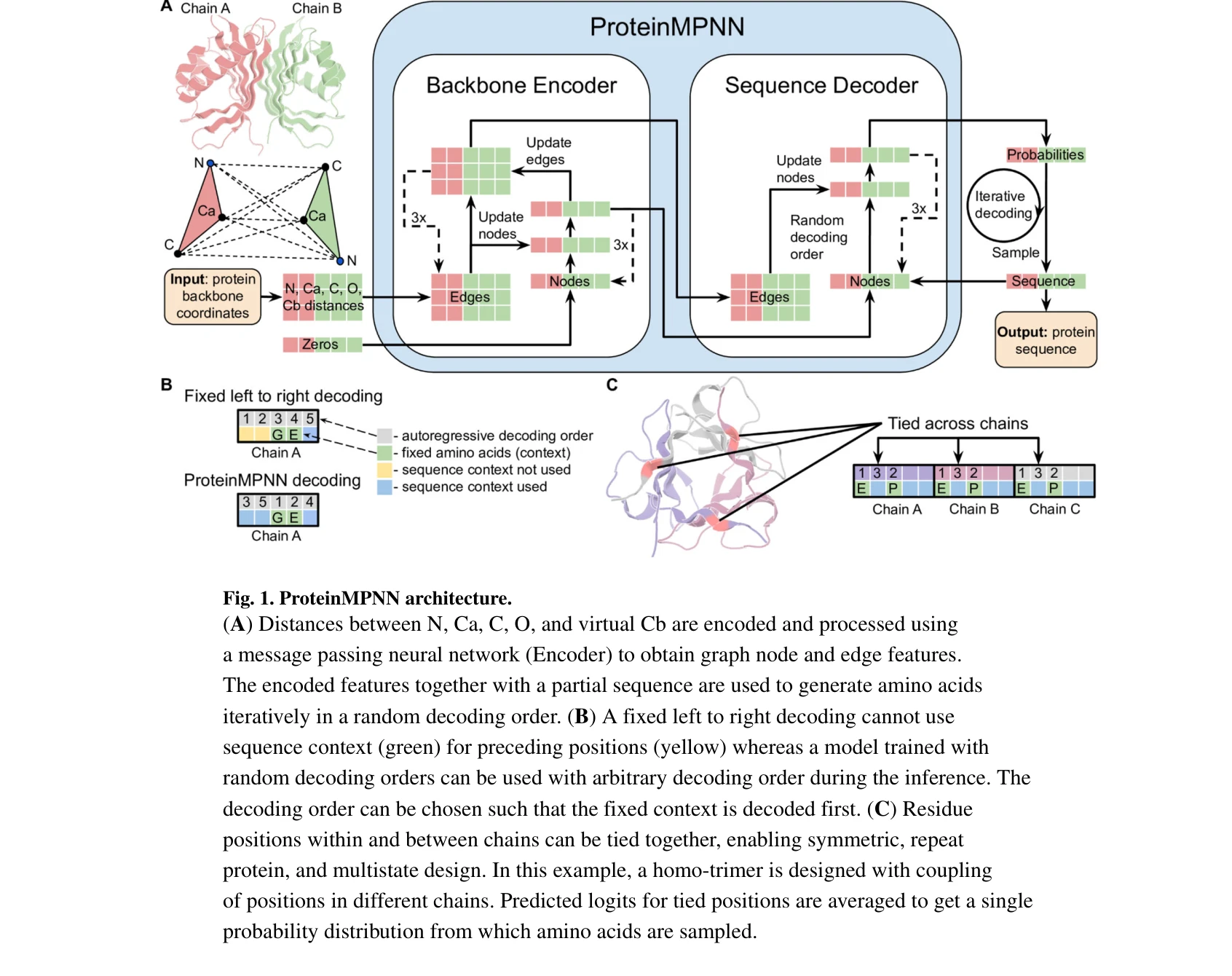
ProteinMPNN 아키텍처: 메시지 패싱 신경망(MPNN) 기반의 순서-비의존적 자가회귀 모델로, 다중 체인 및 대칭성을 고려한 위치 결합 설계 가능
깊은 신경망 기반 단백질 서열 설계 방법 ProteinMPNN을 개발하여, 기존의 물리 기반 방법(Rosetta)보다 우수한 성능을 보이며 다양한 단백질 설계 문제에 광범위하게 적용 가능함을 입증했다.
저자: J. Dauparas, I. Anishchenko, N. Bennett, H. Bai, R. Ragotte | 날짜: 2022 | DOI: 10.1126/science.add2187

ProteinMPNN 아키텍처: 메시지 패싱 신경망(MPNN) 기반의 순서-비의존적 자가회귀 모델로, 다중 체인 및 대칭성을 고려한 위치 결합 설계 가능
깊은 신경망 기반 단백질 서열 설계 방법 ProteinMPNN을 개발하여, 기존의 물리 기반 방법(Rosetta)보다 우수한 성능을 보이며 다양한 단백질 설계 문제에 광범위하게 적용 가능함을 입증했다.
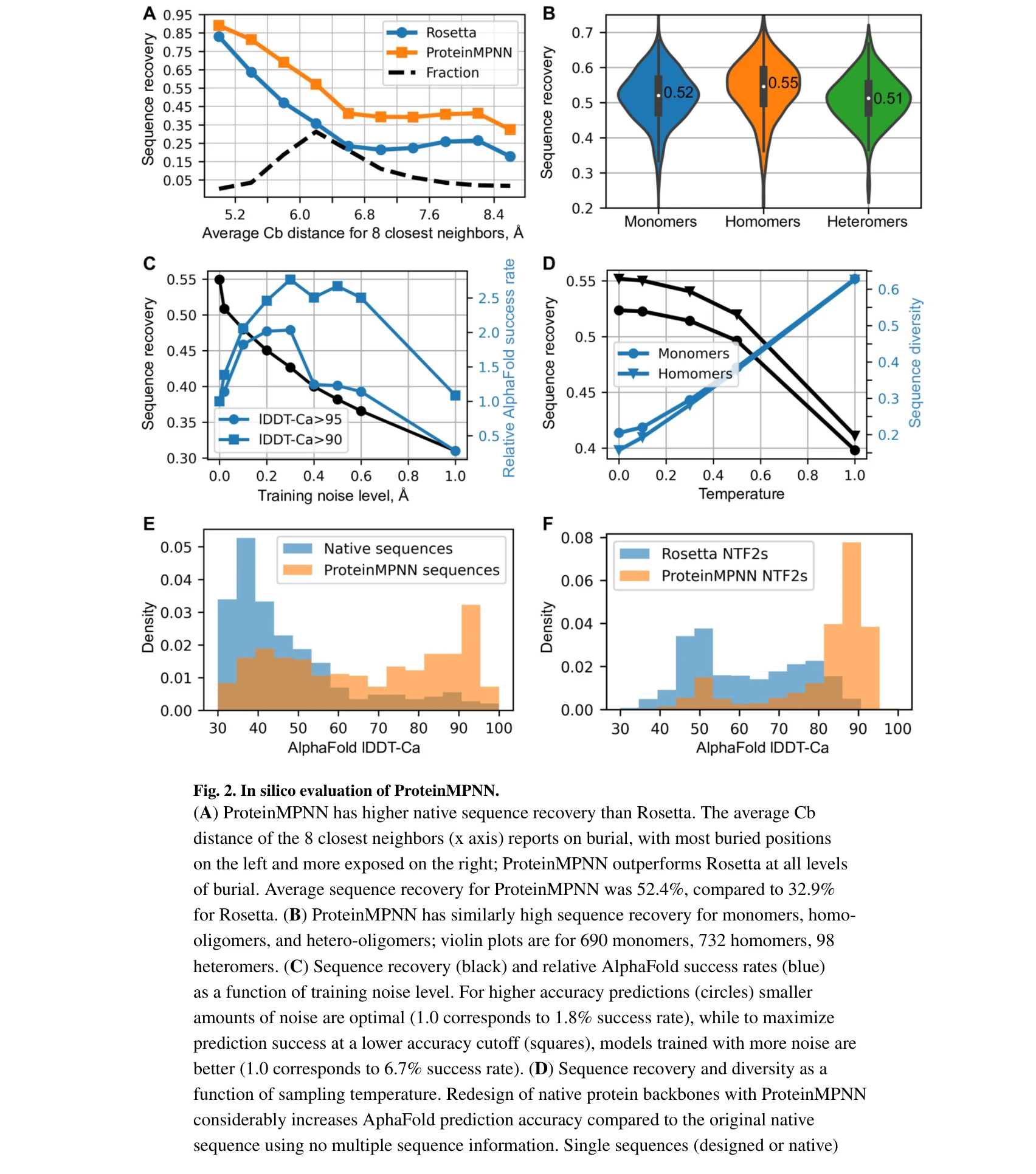
ProteinMPNN의 전산 평가: (A) Rosetta 대비 월등한 서열 복구율(52.4% vs 32.9%), (B) 모노머(52%), 호모머(55%), 헤테로머(51%) 중위 서열 복구율, (C) 백본 노이즈 추가 학습의 영향, (E) 단일 서열 AlphaFold 예측에서 ProteinMPNN 서열의 우수한 구조 부호화

ProteinMPNN 모델 아키텍처의 주요 개선 사항
아키텍처 개선:
순서-비의존적 자가회귀 모델:
다중 체인 및 대칭성 인식:
학습 설정:
한계:
후속 연구 방향:
총평: ProteinMPNN은 깊은 학습 기반 단백질 설계에서 기존 물리 기반 방법의 한계를 혁신적으로 극복한 작업으로, 순서-비의존적 자가회귀와 견고성 중심의 학습 철학이 핵심이며, 모노머부터 올리머, 나노입자까지 광범위한 실용적 적용 가능성을 갖춘 분야 선도적 연구다.