Essence
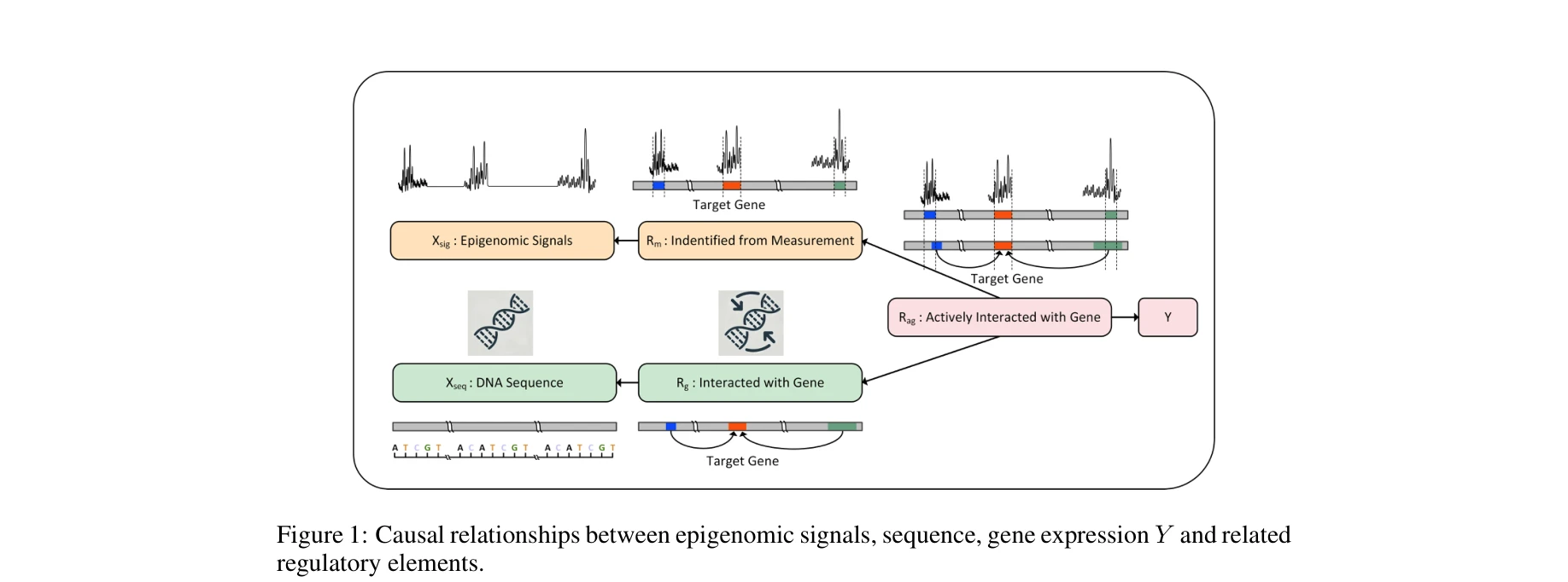
그림 1: 에피지노믹 신호, DNA 서열, 유전자 발현 Y 및 관련 조절 요소 간의 인과관계
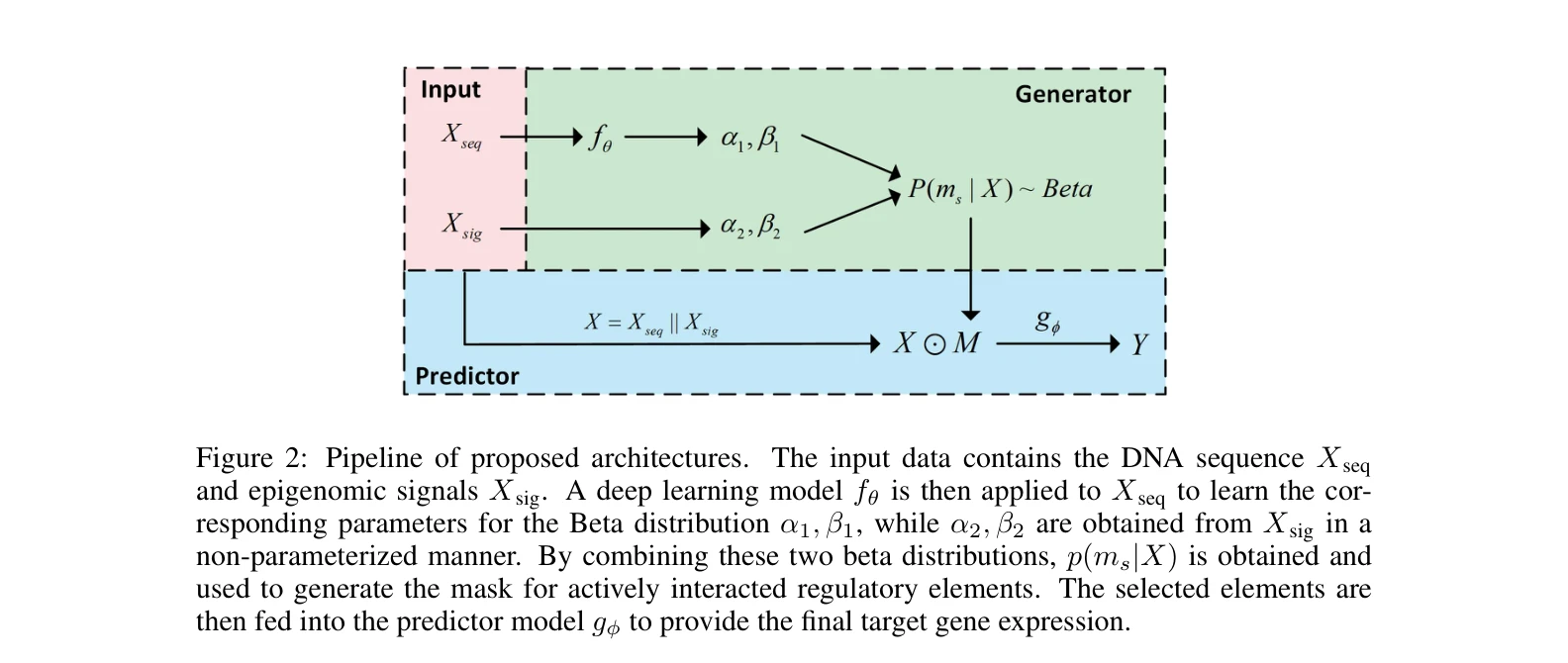
본 논문은 DNA 서열과 에피지노믹 신호로부터 유전자 발현을 예측하되, 능동적으로 상호작용하는 조절 요소(regulatory elements)를 자동으로 발견하는 Seq2Exp 프레임워크를 제안한다. 정보 병목(information bottleneck) 원리를 활용하여 인과적 조절 요소만을 추출함으로써 기존 방법들을 능가하는 성능을 달성한다.