Essence

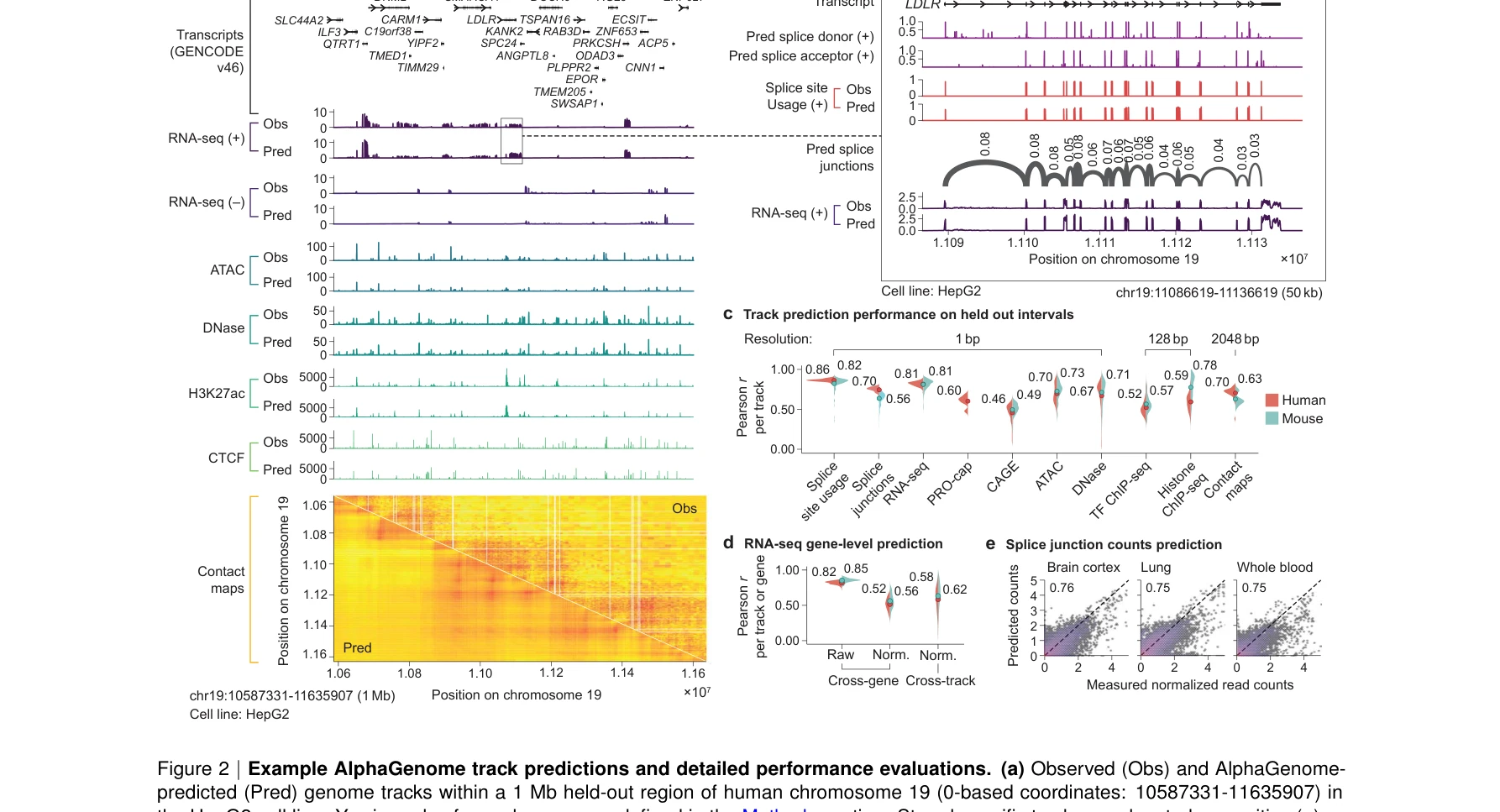
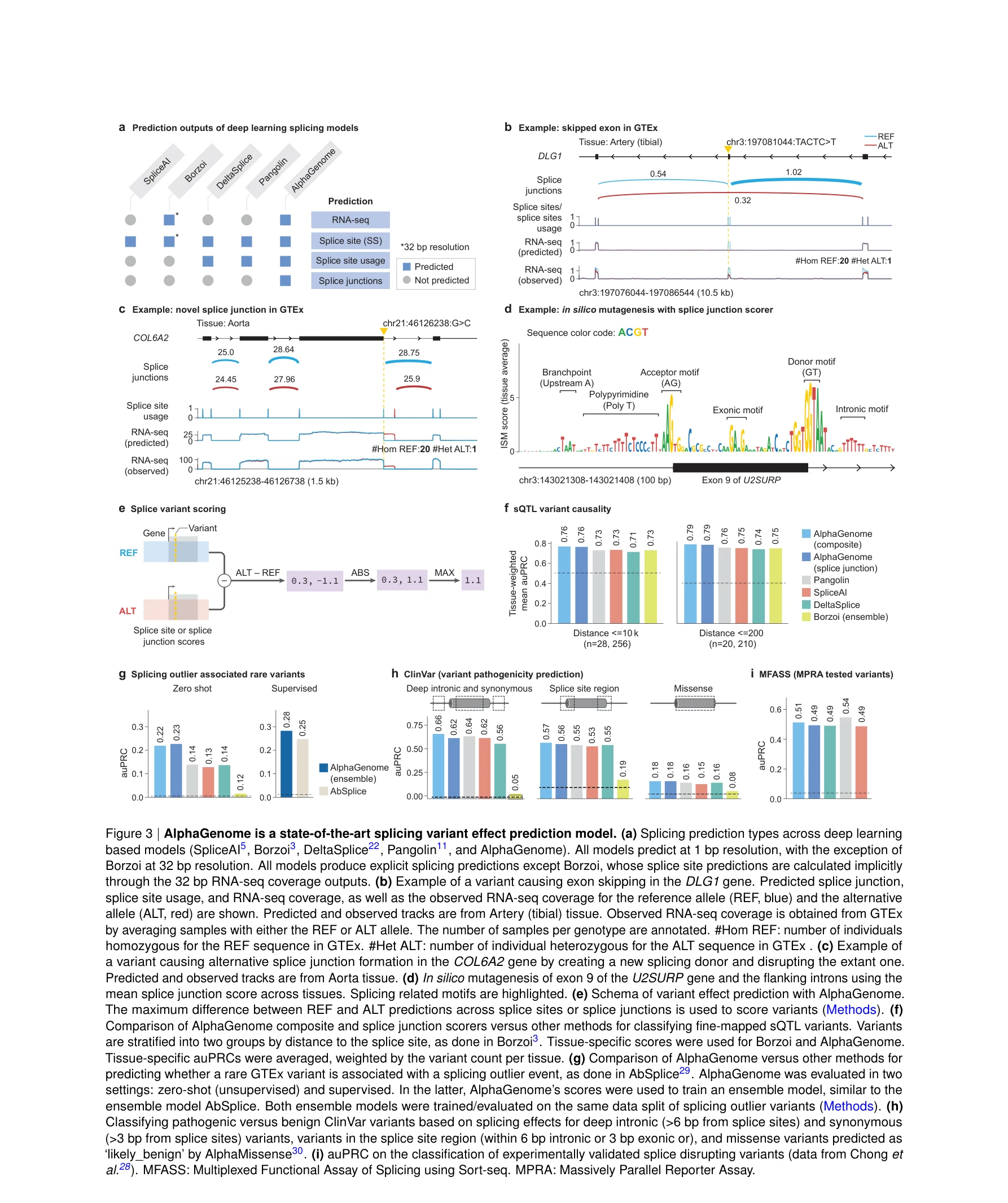
Figure 1: AlphaGenome 모델 아키텍처, 학습 방식 및 종합 평가 성능. (a) 모델 개요: 1 Mb DNA 서열을 입력받아 11개 모달리티에서 5,930개의 게놈 트랙을 단일 염기쌍 해상도로 예측. (e) 변이 효과 예측에서 기존 모델 대비 상대적 성능 개선
AlphaGenome은 1 메가베이스(Mb) DNA 서열 입력과 단일 염기쌍(bp) 해상도를 통합하여, 11개의 생물학적 모달리티(유전자 발현, 스플라이싱, 크로마틴 접근성, 조직인자 결합, 3D 크로마틴 구조 등)에 걸쳐 5,930개의 게놈 트랙을 동시에 예측하는 통합 딥러닝 모델이다.