저자: Sepideh Maleki, Jan-Christian Huetter, Kangway V. Chuang, David Richmond, Gabriele Scalia, Tommaso Biancalani (Genentech) | 날짜: 2024 | DOI: N/A
Essence
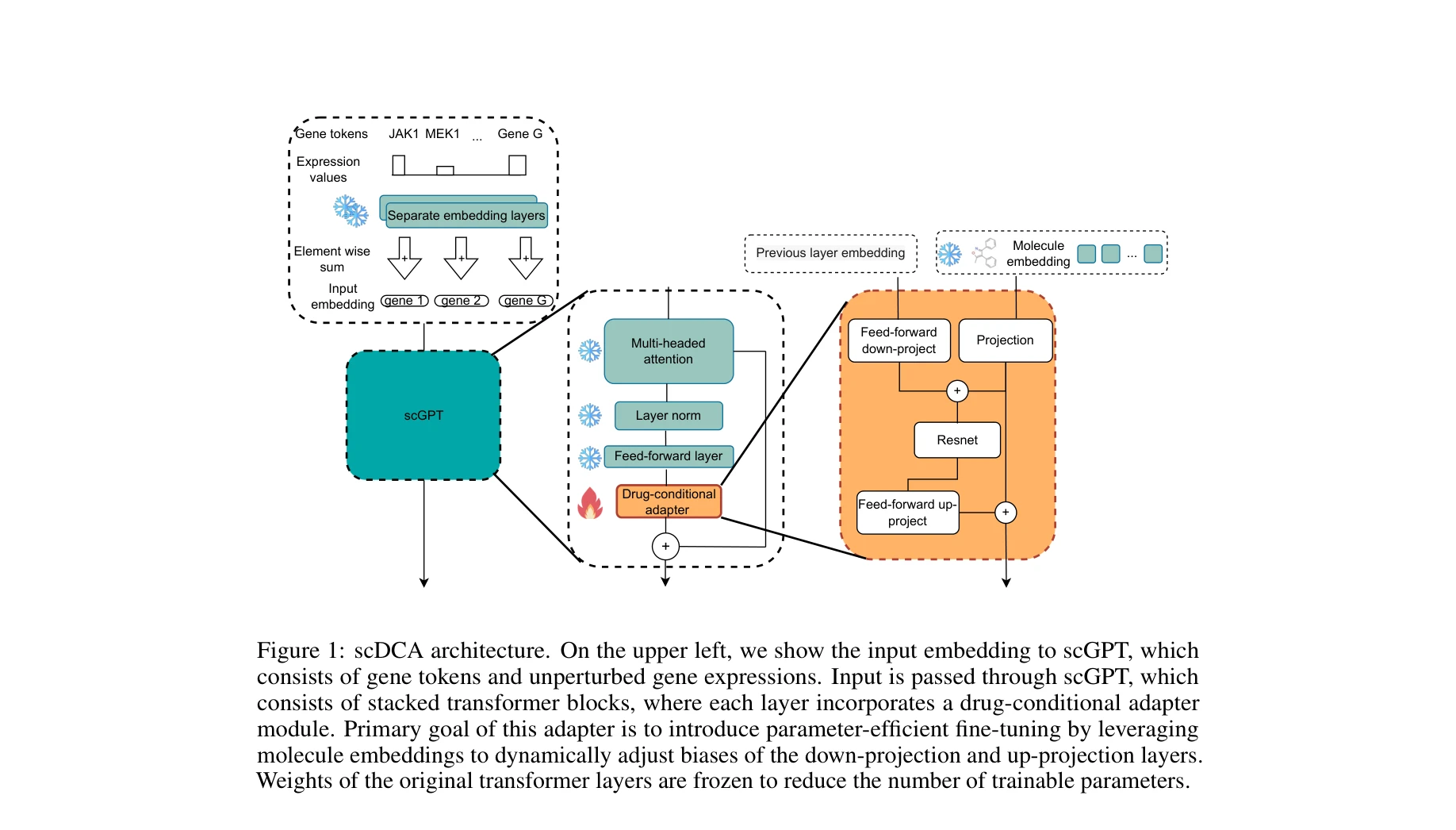
scDCA 아키텍처: scGPT의 각 transformer 블록에 drug-conditional adapter를 통합하여 분자 임베딩으로 동적으로 down-projection과 up-projection 계층의 편향을 조정
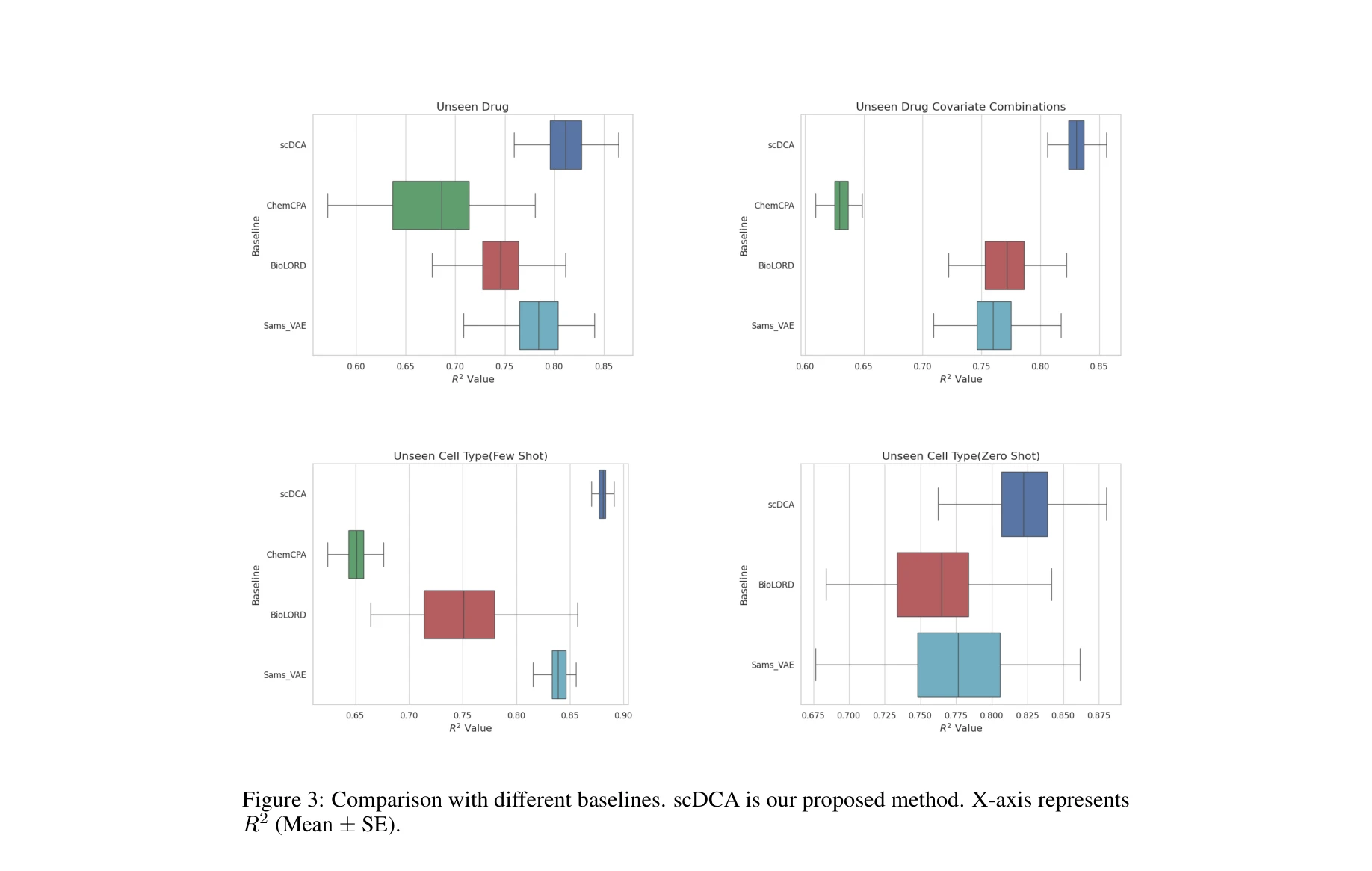
단일세포 기초 모델(foundation model)을 약물 조건부 어댑터(drug-conditional adapter)로 효율적으로 미세조정하여, 미래 약물에 대한 세포 반응 예측 및 미보유 세포주(unseen cell line)에 대한 제로샷 일반화를 가능하게 한다.
Evaluation
Novelty: 4.5/5 Technical Soundness: 4/5 Significance: 4.5/5 Clarity: 4/5 Overall: 4.25/5
총평: 이 논문은 단일세포 기초 모델을 약물 발견에 적용하기 위한 실질적이고 우아한 해결책을 제시하며, 특히 미보유 세포주에 대한 zero-shot 예측 능력과 파라미터 효율성 측면에서 현저한 기여를 한다. 다만 분자 임베딩 전략, 예측 메커니즘 해석, 그리고 임상 타당성 검증 강화가 향후 연구의 중요한 과제이다.