저자: Haonan Zhu, Mary Silva, Jose Cadena, Braden C. Soper, Michal Lisicki, Braian Peetoom, Sergio Baranzini, Shivshankar Sundaram, P. Ray, J. Drocco | 날짜: 2025 | DOI: 미제공
Essence

Deep Active Learning 프레임워크의 전체 흐름: SPOKE 지식 그래프에서 생성된 유전자 임베딩을 초기화하고, 신경망을 통해 상호작용을 예측하며, 획득함수 기반 능동학습 루프로 다음 탐사 대상 유전자 쌍을 선정
본 논문은 HIV 감염에서 숙주 유전자 쌍의 시너지 상호작용을 효율적으로 발견하기 위해 생물학적 지식 그래프(SPOKE)와 딥러닝 기반 능동학습(Deep Active Learning, DeepAL)을 통합한 프레임워크를 제시한다. 356개 유전자의 상호작용 공간(356×356 행렬)에서 실험 비용을 최소화하면서 효과적인 이중 녹다운(double knockdown) 쌍을 발견한다.
Evaluation
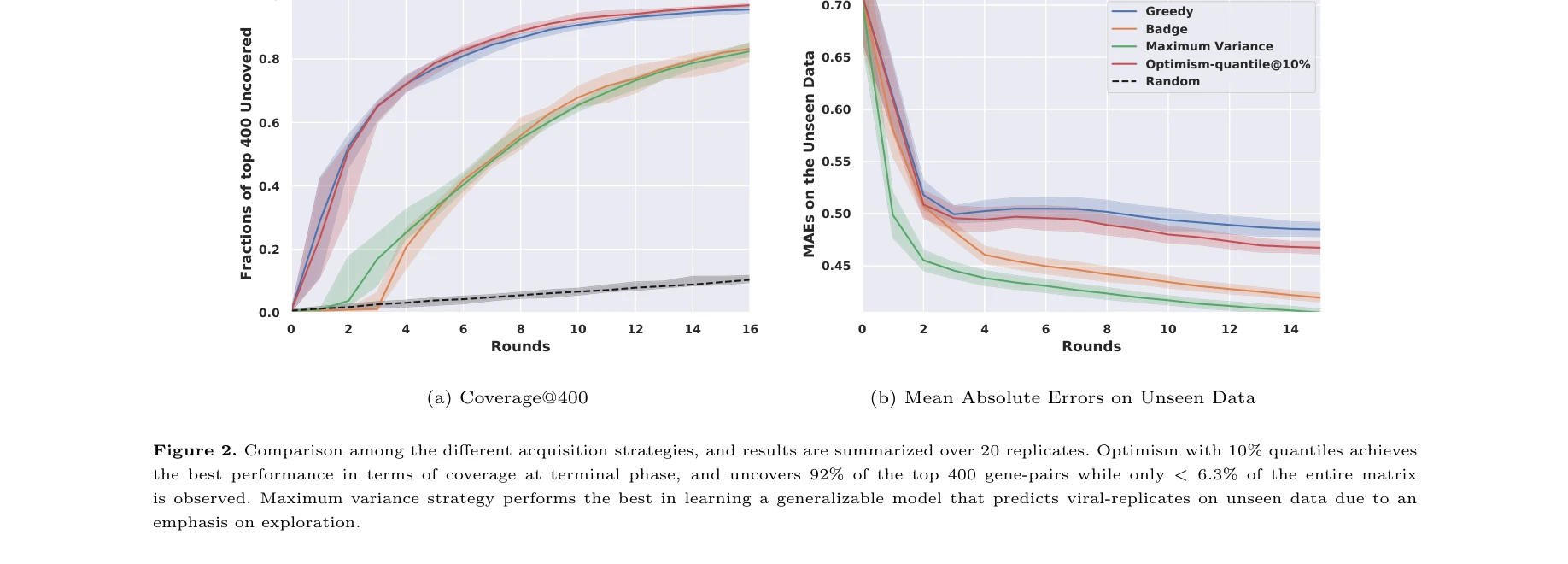
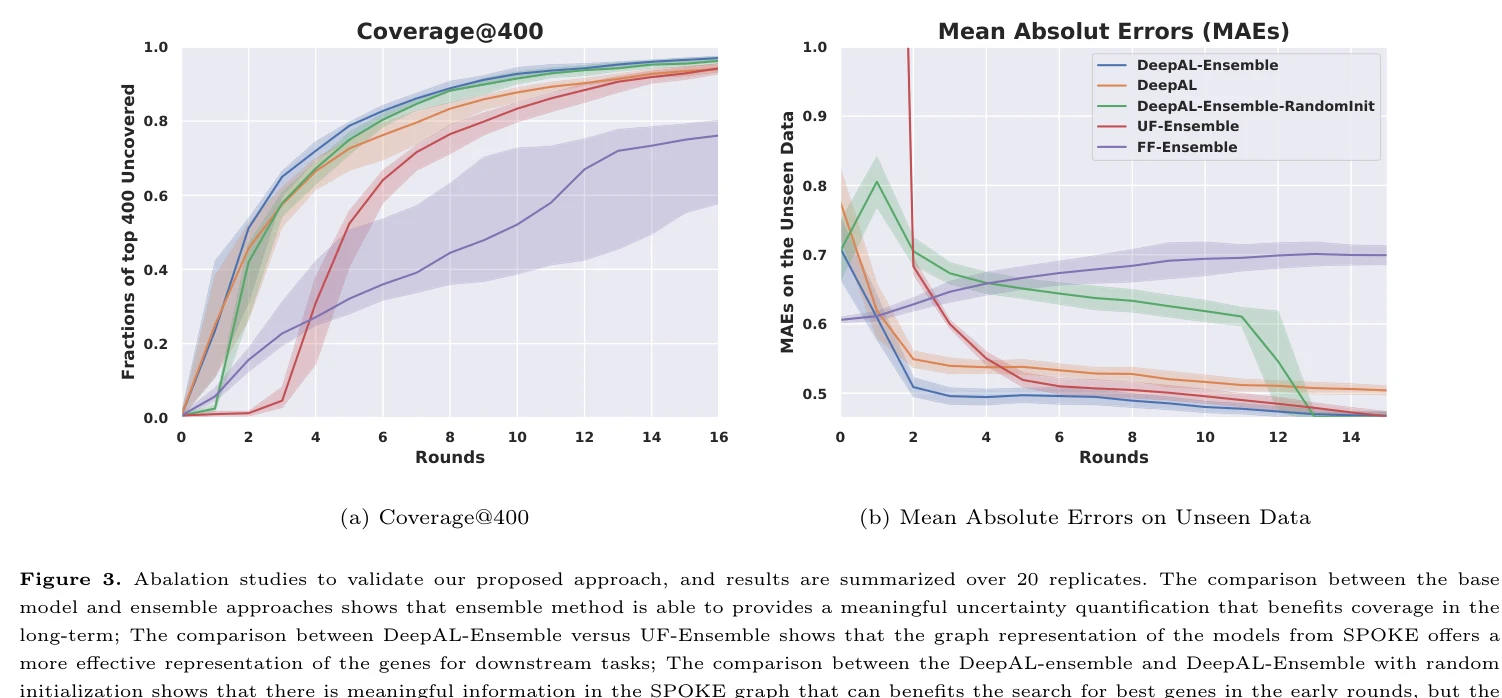
총평: 본 논문은 생물학적 지식 그래프와 딥러닝 능동학습을 효과적으로 통합하여 대규모 유전자 상호작용 공간을 효율적으로 탐색하는 실용적이고 혁신적인 프레임워크를 제시한다. 특히 356×356 규모의 이중 녹다운 데이터 처리는 이 분야에서 획기적이며, 경로 분석을 통한 생물학적 해석가능성도 강점이다. 다만 실제 실험실 검증, 계산 효율성 분석, 그리고 다양한 질병 시스템에의 일반화 가능성에 대한 추가 연구가 필요하다.