Achievement

그림 1: Enformer는 200 kb 입력 서열에서 128 bp 해상도로 게놈 트랙을 예측하며, Transformer 모듈을 통해 Basenji2 대비 5배 큰 수용장(100 kb vs 20 kb)을 달성
- 예측 정확도 획기적 향상: CAGE(Cap Analysis Gene Expression)를 통한 RNA 발현 예측에서 평균 상관계수가 0.81에서 0.85로 증가 (Basenji1→Basenji2 개선의 2배 규모, 실험 수준 정확도 0.94와의 격차 1/3 해소)
- 장거리 규제 요소 통합: 수용장을 20 kb에서 100 kb로 확대함으로써 고신뢰도 인핸서-유전자 쌍의 포함 비율을 47%에서 84%로 증가
- 세포 유형 특이성 향상: 조직 또는 세포 유형 특이성 예측이 개선되었으며, 밀접하게 관련된 샘플들에서도 우수한 성능 발휘
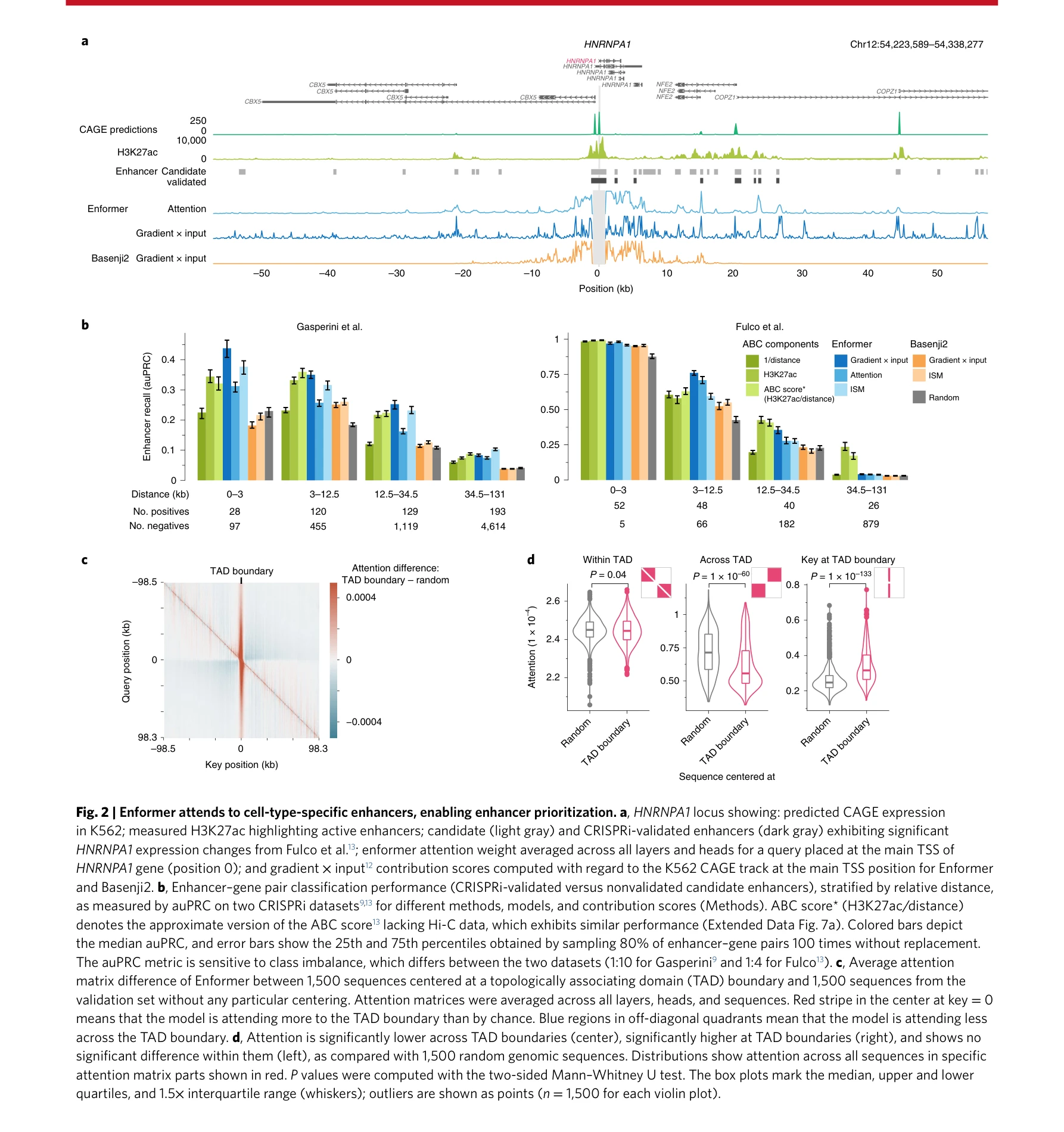
그림 2: Enformer의 기여도 점수가 세포 유형 특이적 인핸서를 식별하며, ABC 점수와 필적하는 인핸서 우선순위화 성능 달성
- 인핸서 우선순위화: DNA 서열만을 입력으로 하면서도 실험 데이터(HiC, H3K27ac)를 사용하는 ABC 점수와 동등하거나 더 우수한 성능으로 인핸서-유전자 상호작용 예측
- 절연체 요소 학습: 위상 연관 영역(TAD) 경계에 대한 주목이 임의의 위치보다 높고, 경계 반대편 영역에 대한 주목이 낮은 패턴으로 절연체 기능 학습 확인