Essence
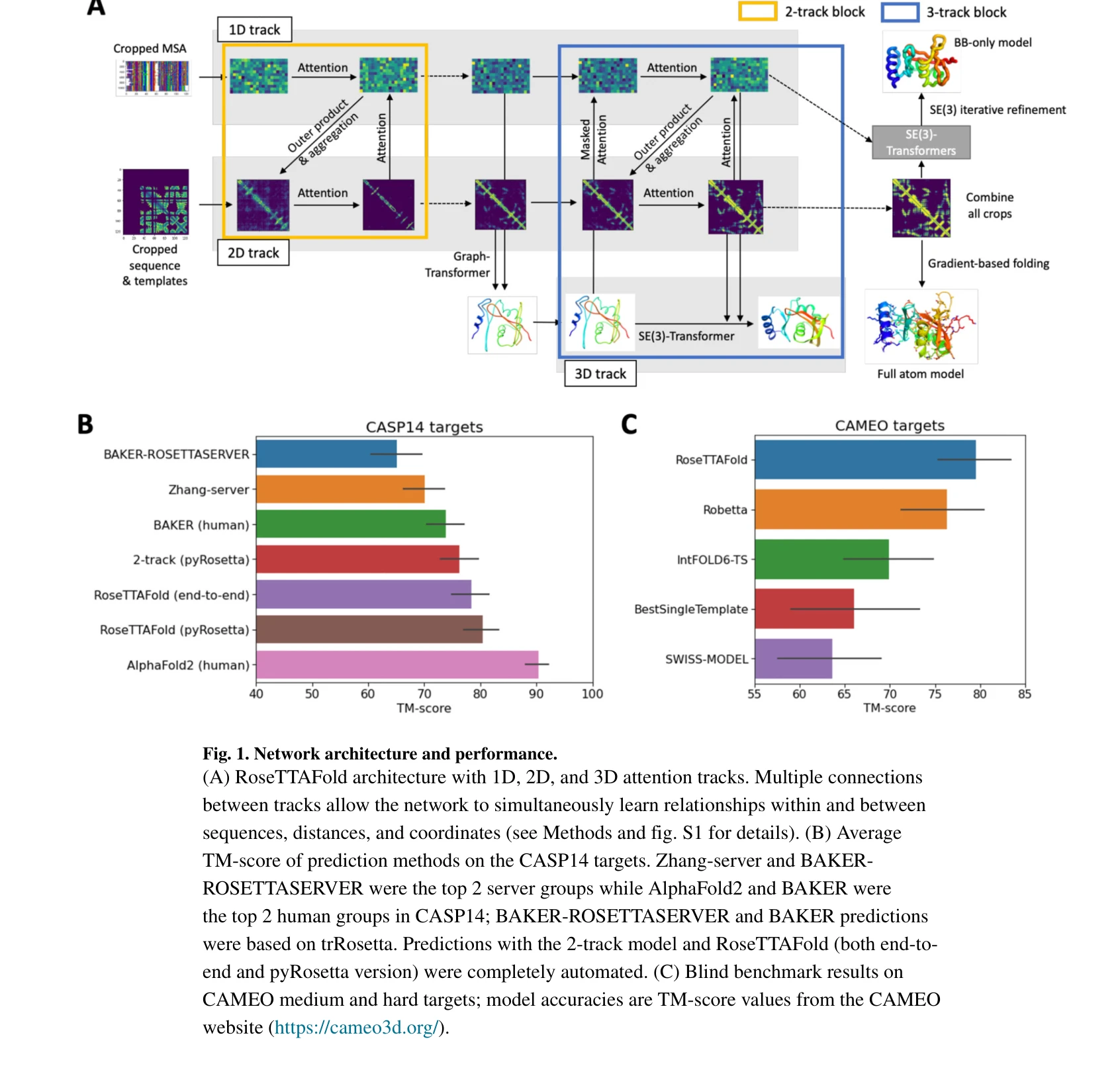
Fig. 1. Network architecture and performance.
3-트랙 신경망 아키텍처를 이용하여 1D 서열, 2D 거리 지도, 3D 좌표 정보를 동시에 처리함으로써 AlphaFold2에 근접한 단백질 구조 예측 정확도를 달성하고 단백질-단백질 복합체 모델링을 가능하게 했다.
저자: Minkyung Baek, Frank DiMaio, Ivan Anishchenko, Justas Dauparas, Sergey Ovchinnikov, Gyu Rie Lee, Jue Wang, Qian Cong, Lisa N. Kinch, R. Dustin Schaeffer, Claudia Millán, Hahnbeom Park, Carson Adams, Caleb R. Glassman, Andy DeGiovanni, Jose H. Pereira, Andria V. Rodrigues, Alberdina A. Van Dijk, Ana C. Ebrecht, Diederik J. Opperman, Theo Sagmeister, Christoph Buhlheller, Tea Pavkov-Keller, Manoj K. Rathinaswamy, Udit Dalwadi, Calvin K. Yip, John E. Burke, K. Christopher Garcia, Nick V. Grishin, Paul D. Adams, Randy J. Read, David Baker | 날짜: 2021-08-20 | DOI: 10.1126/science.abj8754

Fig. 1. Network architecture and performance.
3-트랙 신경망 아키텍처를 이용하여 1D 서열, 2D 거리 지도, 3D 좌표 정보를 동시에 처리함으로써 AlphaFold2에 근접한 단백질 구조 예측 정확도를 달성하고 단백질-단백질 복합체 모델링을 가능하게 했다.
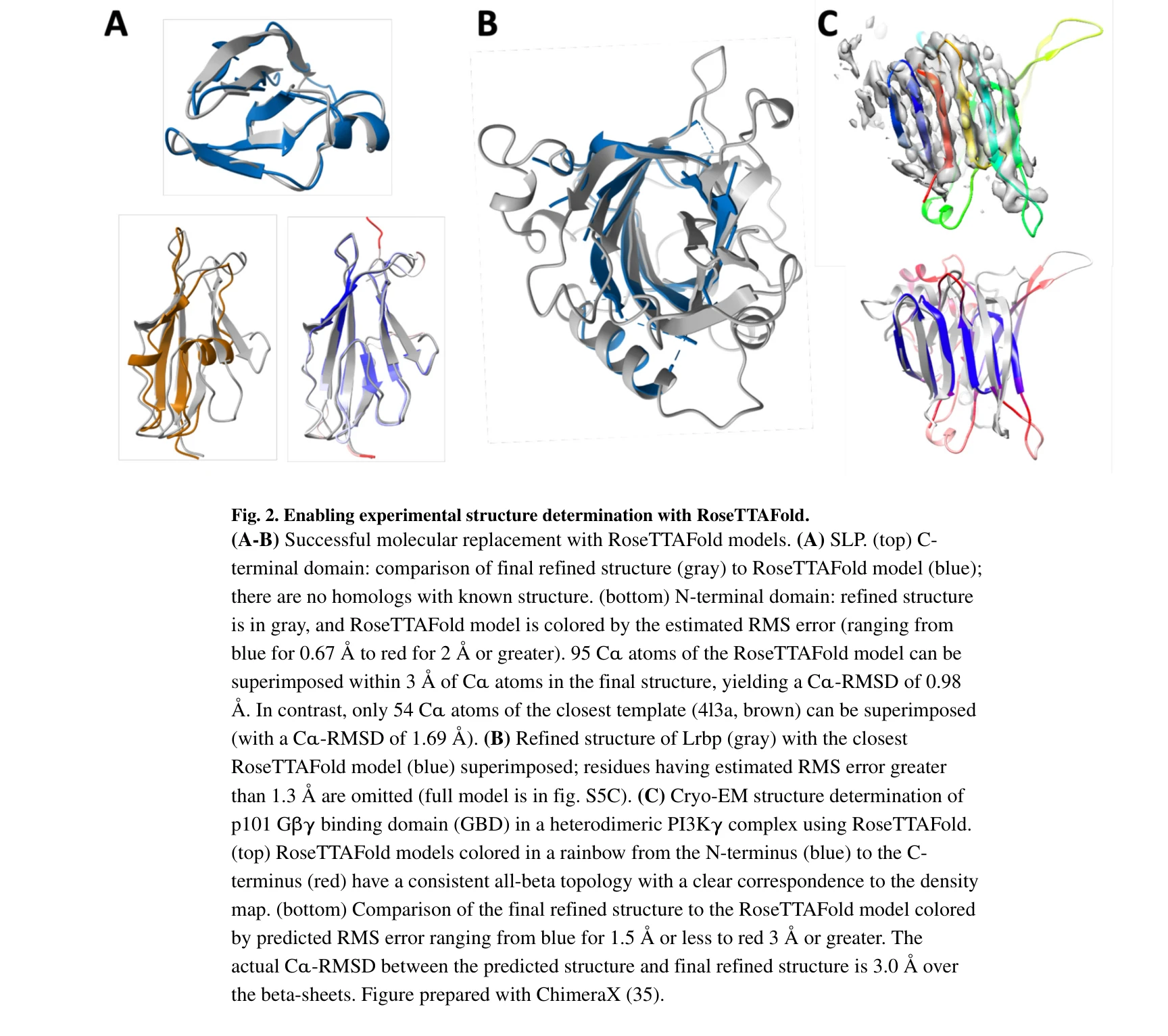
Fig. 2. Enabling experimental structure determination with RoseTTAFold.

Fig. 1. Network architecture and performance.
총평: RoseTTAFold는 AlphaFold2의 핵심 개념을 3-트랙 아키텍처로 창의적으로 재구성하여 경쟁력 있는 성능을 달성했으며, 특히 공개 방식으로 제공됨으로써 단백질 구조 예측의 민주화와 구조생물학 연구 가속화에 크게 기여하는 획기적인 연구다.